La determinazione dell’ordine dei nucleotidi costituenti una molecola di DNA ha fornito una visione integrale del genoma di molti organismi.
I primi metodi che hanno permesso il sequenziamento delle molecole di acidi nucleici sono stati sviluppati nel 1973 da Allan Maxam e Walter Gilbert e nel 1975 da Frederick Sanger e dai suoi collaboratori. Attualmente, le tecniche di Next Generation Sequencing consentono la determinazione della sequenza di interi genomi in poche settimane.
Nel 1995, su Science, fu pubblicato un articolo in cui veniva spiegato il sequenziamento del genoma del batterio Haemophilus influenzae (immagine 1), un coccobacillo Gram negativo patogeno per l’uomo.
Fu osservato che il genoma di H. influenzae è composto da 1.830.137 coppie di basi e da circa 1.743 geni. Furono indicate le localizzazioni dei siti di riconoscimento per gli enzimi di restrizione Not I, Rsr II e Sma I.
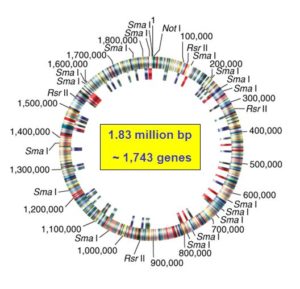
Immagine 1: genoma sequenziato di Haemophilus influenzae
Successivamente la pubblicazione dell’articolo sul sequenziamento del genoma di Haemophilus influenzae, sono stati sequenziati ulteriori genomi batterici, virali, archei ed eucariotici. Ad oggi, sono stati sequenziati i genomi di 276.022 batteri, 2.923 archei e 8.937 virus. Basti pensare che nel giugno 2011 i genomi batterici completamente sequenziati erano 1.200 e 1.300 erano in avanzato stato di sequenziamento; nello stesso anno erano stati sequenziati appena 100 genomi di archei e 76 genomi eucariotici (funghi e protozoi).
L’esponenziale aumento del numero di microrganismi di cui è stato sequenziato il genoma è il risultato di un’evoluzione delle tecnologie di robotizzazione e di miniaturizzazione che hanno permesso la riduzione dei tempi e dei costi dei metodi di sequenziamento.
L’avvento del sequenziamento dell’intero genoma della cellula di Haemophilus influenzae ha reso possibile una rivoluzione importante nei campi della biologia molecolare e della genetica: invece di studiare la struttura e la funzione di un singolo gene o, comunque, di un numero limitato di geni contemporaneamente, è possibile osservare ed esaminare l’insieme dei geni e della componente non codificante del materiale genetico di una cellula. Si possono, quindi, stabilire, grazie alla relativamente nuova disciplina denominata genomica, le interazioni tra le porzioni codificanti e le porzioni non codificanti del genoma intuendo una importante attività di queste ultime nella regolazione dell’espressione genica. L’insieme dei trascritti e l’insieme dei prodotti della traduzione, le proteine, possono essere altrettanto studiati ed esaminati nella loro completezza grazie alle discipline denominate trascrittomica e proteomica, rispettivamente. L’insieme delle cosiddette scienze omiche, che riguardano anche altri aspetti della biologia (metabolomica, relativa agli studi sui metaboliti presenti in una cellula), forniscono un punto di vista alternativo alla genetica classica che rende ancora più affascinante lo studio della biologia.
Per un aggiornamento sui genomi già sequenziati e in stato avanzato di sequenziamento è possibile consultare la banca dati GOLD Genomes online, https://gold.jgi.doe.gov/.
Introduzione alla genomica http://ddlab.sci.univr.it/alberto/bioinformatica/Teoria_L09_Introduzione%20alla%20Genomica.pdf
Whole-genome random sequencing and assembly of Haemophilus influenzae Rd. Fleischmann RD, Adams MD, White O, Clayton RA, Kirkness EF, Kerlavage AR, Bult CJ, Tomb JF, Dougherty BA, Merrick JM, et al. Science. 1995.
Biologia dei microrganismi. Gianni Dehò e Enrica Galli. Casa editrice Ambrosiana. 2016. Pag. 489 – 490.
Immagine 1 da Genetics: analysis and principles. https://slideplayer.com/slide/2777287/
Immagine in evidenza da La ingeniería: al servicio de mejorar la calidad humana. https://www.ingenieria.es/mejorar-la-calidad-humana/