Cosa sono le banche del DNA?
Quando pensiamo ad una banca ci viene subito in mente la struttura fisica in cui preleviamo o depositiamo i soldi. In realtà questo non è l’unico sistema bancario esistente: in biologia molecolare le banche del DNA sono una raccolta di frammenti di DNA, inseriti in specifici vettori, che rappresentano un organismo.
Esistono di due tipologie di banche del DNA: banche genomiche e banche di cDNA (DNA complementare). Entrambe vengono costruite mediante un processo comune: estrazione delle molecole, trattamento del DNA con enzimi di restrizione e l’inserimento dei frammenti ottenuti in appositi vettori.
Enzimi di restrizione
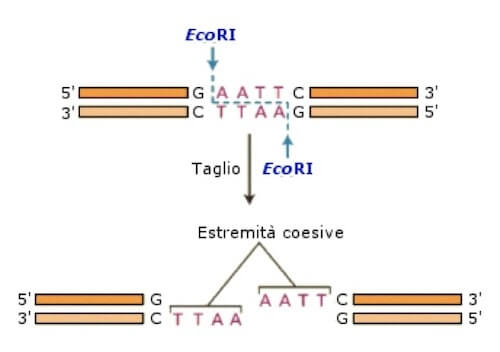
Prima di entrare nel dettaglio è utile sapere cosa sono e come funzionano gli enzimi di restrizione. Un enzima di restrizione è un endonucleasi di origine batterica, taglia cioè all’interno del DNA rompendo il legame fosfodiesterico tra due nucleotidi. Ciò che rende però veramente speciali questi enzimi è la loro specificità: un enzima di restrizione taglierà solo a livello di una specifica sequenza consensus rappresentata a sua volta da sequenza palindromica.
Ogni enzima di restrizione avrà quindi la propria sequenza corrispondente e diversi enzimi di restrizione taglieranno in punti diversi del genoma.
Inoltre, come vedremo in seguito, l’azione di questi enzimi ci permette di realizzare molecole ricombinanti. Effettuando infatti la digestione di due DNA con lo stesso enzima, potremo ottenere molecole con estremità coesive capaci quindi di legarsi.
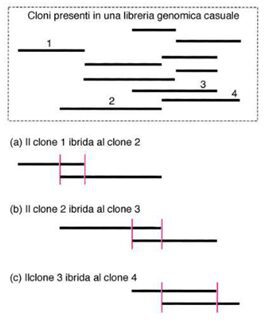
Costruzione di una libreria di DNA genomica
Come già accennato, i primi due passaggi consistono nell’estrazione del DNA e nel trattamento di esso con enzimi di restrizione. La digestione effettuata è però una digestione di tipo parziale, ovvero una digestione in cui non tutti i siti di restrizione vengono tagliati. Come conseguenza otterremo dei frammenti parzialmente sovrapponibili, ovvero frammenti che conterranno sequenze in parte complementari.
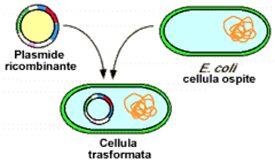
A questo punto ogni frammento verrà inserito in uno specifico vettore, che nel caso più semplice è rappresentato da un plasmide. A sua volta quest’ultimo verrà inserito in una cellula batterica mediante trasformazione.
La generazione di frammenti parzialmente sovrapponibili sarà utile nel processo di ricostruzione del genoma: preso un primo frammento parte di esso potrà essere utilizzato come sonda al fine di individuare il frammento consecutivo e così via.
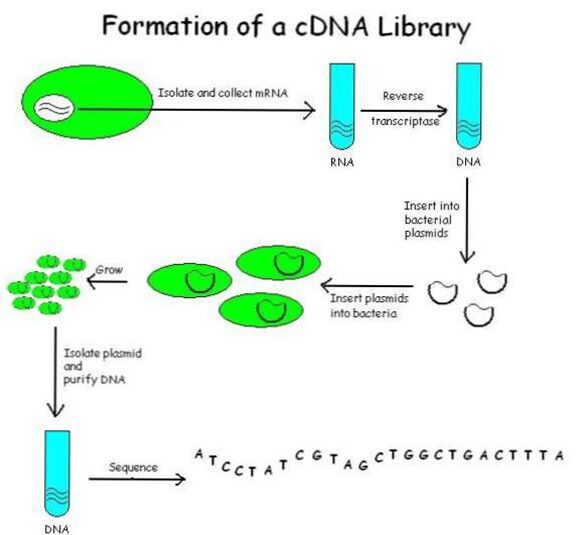
Costruzione di una libreria di cDNA
Il cDNA o DNA complementare è il risultato della retrotrascrizione del mRNA mediante la trascrittasi inversa. Dunque, una volta che il DNA viene trascritto, un enzima compie il processo inverso trasformando nuovamente l’RNA in DNA. Ma come si attua il processo di retrotrascrizione?
- l’RNA viene purificato dal materiale biologico di interesse;
- L’mRNA viene separato dagli altri RNA: si sfrutta una sonda molecolare composta da nucleotidi di timina (oligo-T) che individua per complementarietà la coda poli-A che contraddistingue ogni mRNA;
- Gli stessi oligo-T legati svolgono anche la funzione di primer per la trascrittasi inversa che sintetizza un filamento di c-DNA. Si forma quindi la molecola ibrida RNA/cDNA;
- Si sottopone la molecola all’azione dell’RNAsi che rompe il doppio filamento. Piccoli frammenti di RNA rimangono comunque legati al cDNA e vengono utilizzati come inneschi per la sintesi del filamento complementare.
A questo punto non ci resta che inserire i frammenti ottenuti all’interno dei plasmidi. Affinché questo possa avvenire aggiungiamo alle estremità dell’cDNA i cosiddetti adattatori o linkers, ovvero pezzi di DNA che contengono siti riconosciuti da enzimi di restrizione. Digeriamo quindi sia il cDNA che il plasmide con lo stesso enzima di restrizione e realizziamo la nostra molecola ricombinante.
Infine, ancora una volta, i plasmidi verranno inseriti per trasformazione nella cellula ospite.
Conclusioni
In conclusione, una banca genomica è una raccolta di frammenti di DNA che portano l’informazione dell’intero genoma, mentre una banca di cDNA è una raccolta di frammenti di DNA ottenuti mediante retrotrascrizone.
È importante sottolineare che nel secondo caso l’utilizzo di mRNA permette di evidenziare l’espressione genica di una data popolazione cellulare in un dato momento. Inoltre, una banca di cDNA, non contenendo sequenze introniche, è relativamente più piccola, mentre una banca di DNA, che contiene tutto il genoma (anche le sequenze non codificanti), costituisce una banca ben più grande.
Fonti
- https://it.sawakinome.com/articles/biology-science-nature/difference-between-cdna-and-genomic-library.html
- Libri: Genetica di Pierce, Genetica dall’analisi formale alla genomica di Hartwell