Quanto DNA è presente in una cellula? Come fa a starci tutto? È vero che all’aumentare della complessità di un organismo aumenta anche la quantità di DNA e di geni?
Come si nota dall’immagine copertina di questo articolo, la quantità di DNA in una cellula è piuttosto abbondante. Nello specifico l’immagine rappresenta un ceppo di Escherichia coli K-12 trattato con un detergente blando in modo da far fuoriuscire il DNA senza distruggerlo. La lunghezza di quella lunga cosa filamentosa tutt’attorno a E. coli è di 4,6 Mb (megabasi), ovvero 4,6 milioni di paia di basi. Se distendessimo questo DNA in linea retta, sarebbe lungo circa 1,4 mm…ma riesce a stare all’interno del batterio stesso, grande appena 1 µm!
Se consideriamo poi una cellula umana (decisamente più grande, da 10 a 100 volte rispetto a E. coli), il DNA che troviamo raggiunge la bellezza di 3,1 Gb (gigabasi), ovvero 3,1 miliardi di basi (per genoma aploide): se immaginassimo di distendere tutto questo DNA in linea retta raggiungeremmo i 2 metri…ma una cellula umana media è grande non più di 50 µm!
Eppure, tutto questo materiale genetico ci sta comodo comodo all’interno della cellula, anzi, all’interno del solo nucleo (nel caso di cellule eucariotiche), o in corrispondenza del nucleoide se parliamo di cellule procariotiche. Come? In maniera compatta, la risposta sembra scontata! Infatti, il DNA non è mai da solo potremmo dire, perché viene avvolto attorno a proteine istoniche o simil-istoniche (nel caso di procarioti) che rendono possibile un impacchettamento estremamente efficiente, limitando la repulsione elettrostatica dei gruppi fosfato del DNA e compattandolo nelle strutture note come cromosomi (Fig. 1).

A questo punto sembra lecito domandarsi se la quantità di geni, cromosomi e DNA in generale aumenta con la complessità di un organismo…ma la risposta qui è meno scontata di prima ed è no. Ci si trova davanti ai cosiddetti tre paradossi della genomica:
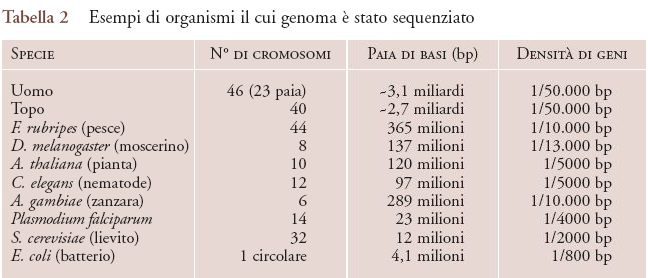
- Paradosso C: la complessità di un organismo non è correlata alla grandezza del suo genoma.
- Paradosso K: la complessità di un organismo non è correlata al numero dei suoi cromosomi.
- Paradosso N: la complessità di un organismo non è correlata al numero dei suoi geni.
Non siete convinti? Date un’occhiata alla figura 2 qui sotto:



E’ possibile spiegare tutto ciò? Innanzitutto è bene sottolineare come complessità non voglia affatto dire che un organismo è più o meno evoluto di un altro: ad esempio E coli è assolutamente e perfettamente evoluto per adattarsi al suo ambiente e alle sue necessità, anche se potremmo definirlo decisamente meno complesso di un essere pluricellulare quale l’uomo. Molto probabilmente poi stiamo contando la cosa sbagliata, ovvero non sono i tanti geni codificanti per proteine o la lunghezza del genoma a fare la complessità, ma piuttosto il numero di diverse interazioni e livelli di regolazione presenti nel genoma.
Andando ad osservare infatti la densità genica (Fig. 3) di vari organismi quello che salta all’occhio è come, più “complesso” un organismo è, minore è la densità genica. Quello che aumenta quindi non sono per forza il numero di cromosomi, geni o basi, ma il genoma non codificante, la cosiddetta dark matter della genomica, che solo negli ultimi decenni è stata rivalutata per la sua essenziale funzione nei processi di interazione e di regolazione (come ad esempio per lo splicing, gli enhancers, RNAi, lncRNAs, …).
Diversi sono i progetti internazionali rivolti proprio alla comprensione delle varie interazioni e regolazioni che governano la fisiologia cellulare e degli organismi, per cercare di capire sempre più questa complessità e costituire una sorta di enciclopedia degli elementi genomici. Tra questi ad esempio:
– ENCODE – progetto che mira a fornire una mappa dettagliata di tutti gli elementi funzionali del genoma umano
– FANTOM5 – progetto volto a indagare gli elementi genomici che regolano l’enorme diversità tra i vari tipi di cellule del corpo umano
– Genomic Science Project – progetto che cerca di identificare gli elementi genomici molecolari e regolatori di piante e microrganismi nell’ambiente
Roberto Amadio
Bibliografia ed approfondimenti
Credits foto
http://microbiologiatalia.tumblr.com/page/3
https://www.differencebetween.com/difference-between-chromatin-and-vs-nucleosome/
(modifica da) http://www.treccani.it/enciclopedia/la-grande-scienza-genomica-e-postgenomica_%28Storia-della-Scienza%29/