La strada della conoscenza: nuovi approcci molecolari
La diffusione dell’ormai noto SARS-CoV-2, responsabile della malattia denominata COVID-19, ha palesato la necessità impellente di conoscere il virus a fondo per poter mettere in atto strategie di attacco e di difesa. Molti sono i team di ricerca in tutto il mondo che si stanno adoperando per condurre lavori minuziosi e capillari al fine di aggiungere tasselli alla conoscenza a tutto tondo del Coronavirus. Tra questi emerge uno studio, condotto da ricercatori dell’Università di Napoli Federico II e dell’Università di Perugia, che si propone di identificare nuovi possibili approcci molecolari al trattamento dell’infezione da SARS-CoV-2.
Lo studio
Nello studio riportato sulla rivista scientifica bioRxiv in fase di pre-print, condotto da un team formato da ricercatori delle università di Napoli e di Perugia, vengono descritti i numerosi possibili siti di legame della proteina spike (S) del virus SARS-CoV-2, importanti perché la loro occupazione ridurrebbe la capacità infettante del virus.
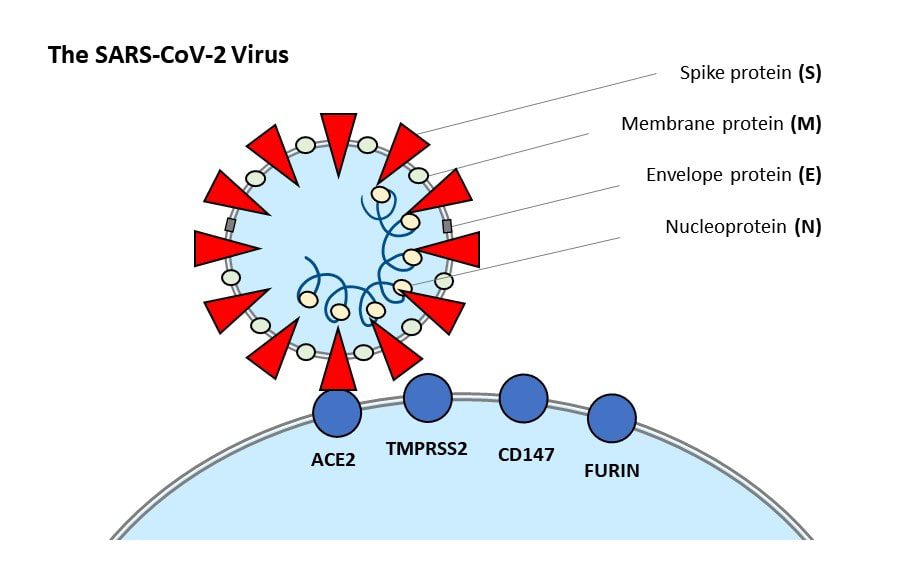
Lo studio si basa sul preconcetto che il virus SARS-CoV-2, per poter infettare l’uomo, deve necessariamente legarsi ad ACE2, un recettore enzimatico di superficie che si trova sulle membrane cellulari delle cellule dei polmoni, delle arterie, del cuore, dei reni e dell’intestino e che rappresenta la porta d’ingresso per il virus stesso. Tale legame è indispensabile affinché un altro enzima, TMPRSS2, divida le subunità S1 e S2 della proteina spike permettendo così alla porzione S2 di effettuare l’aggancio alla membrana cellulare dell’ospite e dare il via al meccanismo molecolare di ingresso del virus.

I ricercatori, effettuando analisi per lo studio del meccanismo d’azione del virus, hanno scoperto che l’organismo per difendersi mette in atto strategie non immunologiche basate sull’utilizzo di molecole endogene.
Molecole endogene di natura steroidea impediscono l’ingresso di SARS-CoV-2 nelle cellule umane
Le molecole endogene di cui si parla nello studio sono di natura steroidea. Esse sono capaci di legare il nucleo centrale del foglio β della porzione RBD della proteina spike impedendo l’ingresso di SARS-CoV-2 nelle cellule umane. Gli studi in silico hanno permesso l’identificazione di sei tasche della porzione RBD che fungono da bersagli per i composti steroidei prodotti naturalmente dall’organismo. In particolar modo, le tasche 1 e 5 sarebbero le più funzionali per l’attacco dell’acido glicirretinico, oleanolico, obeticolico e dei derivati degli acidi biliari glico-UDCA (acido ursodesossicolico).
Gli acidi biliari sono composti prodotti dal fegato derivanti dal colesterolo che vanno a costituire la bile. Quest’ultima, tramite il passaggio nel coledoco, raggiunge successivamente il duodeno in cui svolge numerose funzioni: favorisce il processo digestivo e l’assorbimento di grassi e vitamine liposolubili, permette la neutralizzazione del pH acido delle secrezioni gastriche, stimola la peristalsi intestinale e consente l’eliminazione dei prodotti che derivano dalla degradazione dell’emoglobina e altre sostanze tossiche.

I risultati dello studio hanno anche suggerito che il principale fattore determinante per l’efficacia dell’inibizione è l’idrofobicità. L’acido oleanolico infatti, che si è dimostrato essere l’inibitore più efficace, è privo di qualsiasi interazione di carica all’interno delle tasche interessate della proteina spike.
I limiti dello studio
Lo studio, ancora acerbo ma comunque fondamentale per la conoscenza del virus, presenta alcuni limiti. Innanzitutto, l’approccio farmacologico basato sull’interazione della proteina spike con le molecole endogene prima menzionate, sembrerebbe essere efficace soltanto in situazioni di bassa carica virale. Infatti, si è visto che gli effetti esercitati dal plasma iperimmune ottenuto da pazienti che si sono ripresi da COVID-19, presentano un’elevata inibizione tra porzione RBD di spike e ACE2 dimostrando così che i derivati steroidei sono meno efficaci di un anticorpo neutralizzante.
Inoltre, per questioni legate alle tempistiche, non sono stati visualizzati gli effetti del trattamento sulla replicazione virale.
Conclusioni
In conclusione, i ricercatori del Dipartimento di Scienze Chirurgiche e Biomediche dell’Università di Perugia insieme con i ricercatori del Dipartimento di Farmacia dell’Università degli Studi di Napoli Federico II, hanno così dichiarato:
“I risultati attuali sono una dimostrazione di come il sistema della ricerca universitaria biomedica in Italia sia in grado di produrre risultati utili e di dare soluzioni tempestive a problemi complessi. Dal punto di vista della terapia, sembra probabile che l’approccio sviluppato non consentirà di trattare pazienti con quadri gravi di distress respiratorio, perché gli anticorpi del siero iperimmune ottenuto da pazienti guariti da COVID-19 sono molto più efficaci nell’ inibire il legame tra spike e ACE2. Tuttavia, le sostanze studiate, e altre che speriamo di poter investigare a breve, sono in alcuni casi molecole endogene o farmaci già ampiamente utilizzati da molti anni, con un consolidato profilo di sicurezza, il che ne consentirebbe un uso immediato nei pazienti con COVID-19. Questo approccio potrebbe quindi consentire in modo drastico la riduzione dei tempi per l’esecuzione di trial clinici”.
Fonti
- http://www.unina.it/-/22245970-nuovi-approcci-molecolari-al-trattamento-dellinfezione-da-sars-cov2-covid-19-
- https://www.farmaceuticayounger.science/hotthisweek/hot-this-week-in-farmaceutica-younger-n146/
- https://www.ansa.it/campania/notizie/2020/06/13/coronavirus-scoperta-sostanza-naturale-che-lo-blocca_b0e3c326-bccc-4a5a-ad81-06152bb387b8.html